CLONE AND EXPRESSION ANALYSIS OF INSULIN-LIKE GROWTH FACTOR 3 (IGF3) GENE IN CULTER ALBURNUS
-
摘要: 为研究翘嘴鲌(Culter alburnus Basilewsky)胰岛素样生长因子(Insulin-like growth factor 3, igf3)基因在性别调控过程中的作用, 基于分子克隆手段RT-PCR和RACE技术相结合方法扩增到翘嘴鲌igf3基因完整cDNA序列, 利用qRT-PCR技术检测其在不同组织中的表达水平, 最后通过甲基化检测方法比较分析了翘嘴鲌性腺组织igf3基因组水平的CpG岛修饰水平。实验结果显示igf3 cDNA序列全长901 bp, 包含92 bp的5′端非编码区和203 bp的3′端非编码区, 开放阅读框606 bp, 编码201个氨基酸。序列分析显示, 类似于其他IGF家族成员igf1和igf2, igf3同样存在保守的特征结构域, 主要划分为前体信号肽、B、C、A、D和E区。igf3基因在翘嘴鲌不同组织中的表达水平差异明显(P<0.05), 在卵巢中表达量最高, 其次是精巢组织, 而在脑、心脏、脾脏、肝脏、肌肉和肾脏中表达丰度极低。甲基化检测结果显示在卵巢中CG位点几乎不发生甲基化, 然而精巢中的甲基化程度非常高, 这与其表达水平正好呈负相关。研究结果表明igf3可能参与了性腺的形成或功能维持, igf3基因组启动子区域的DNA甲基化修饰与其在性腺组织的二态性表达特征关系密切。Abstract: Insulin-like growth factors (Igf) are evolutionarily conserved gene family that regulate a variety of cellular biological processes, including growth, proliferation, survival, migration, and differentiation. To understand the role of igf3 gene in sex determination and differentiation in Culter alburnus, the full-length cDNA sequence of igf3 was cloned by rapid amplification of cDNA ends (RACE) technology; real-time quantitative PCR (qRT-PCR) was employed to analyze the expression level of igf3 in different tissues; DNA sequencing of sodium bisulfite was used to explore the CpG methylation pattern of igf3 promoter in adult testes and ovaries. The length of igf3 cDNA was 901 bp with a 92 bp 5′UTR, a 203 bp 3′UTR and a 606 bp ORF encoding of 201 amino acid residues. Sequence analysis showed that similar to other IGF family members igf1 and igf2, igf3 also had conserved characteristic domains, which were mainly divided into precursor signal peptides, B, C, A, D, and E regions. The expression level of igf3 gene was significantly different in various tissues (P<0.05). The expression was the highest in the ovary, followed by the testis, while the expression abundance was extremely low in the brain, heart, spleen, liver, muscle and kidney. Analysis of CpG islands methylation pattern revealed that igf3 promoter CpGs were not methylated in the ovary, but is hypermethylated in the testis. These findings indicated that igf3 was involved in gonadal formation or functional maintenance in C. alburnus, and the DNA methylation modification in the promoter region of igf3 genome was closely related to sexual dimorphism expression between gonadal tissues.
-
Keywords:
- Culter alburnus /
- igf3 /
- Expression analysis /
- DNA methylation
-
鱼类在所有脊椎动物中拥有最复杂的性别决定方式, 不仅存在雌雄同体、雌雄异体和顺序性雌雄同体, 其性别决定类型有遗传调控、环境调控或者两者共同决定的调控方式[1-3]。胰岛素样生长因子(Insulin like growth factors, IGFs)是一类进化上比较保守的基因家族, 调控多种细胞生物学过程, 包括生长、增殖、生存、迁移和分化[4-6]。基于哺乳动物中的研究发现, 胰岛素样生长因子系统包括IGF配体、IGF受体及6种IGF蛋白[7, 8]。当前大量研究证实IGFs家族在鱼类等脊椎动物性腺发育与分化中具有重要作用, 但大多偏向于igf1和igf2基因和受体的研究[9]。2008年有研究者在斑马鱼(Danio rerio)[10]和罗非鱼(Oreochromis niloticus)[11]卵巢中首次分离到一种新颖的IGF类型家族基因(igf3), 随后陆续在斜带石斑鱼(Epinephelus coioides)[12]、双棘黄姑鱼(Protonibea diacanthus)[13]和鲤(Cyprinus carpio)[14]中获得相关序列信息。初步研究证实igf3基因仅在鱼类的卵巢和精巢中特异表达, 并始于性别决定分化早期, 在性腺发育过程中持续高表达。由于igf3基因发现较晚, 目前尽管围绕igf3基因的相关研究逐渐在增多, 但其在鱼类性腺发育中的调控机制仍然不清楚, 有待深入的研究来阐明igf3如何发挥重要的生理学功能。
在鱼类性别决定和性腺分化的过程中, 许多环境因素(如温度、外源激素)可以影响雌雄性别比例或性别分化, 这种性别决定与分化大多依赖于表观遗传调控, 特别是DNA甲基化修饰[15]。大量研究表明许多类固醇合成酶和转录因子的表达受到表观遗传修饰调控, 如在温度依赖的海龟性别分化过程中, 高温处理下重要类固醇合成酶CYP19A在雌性幼龟中的甲基化水平增加, 致使cyp19a基因表达抑制继而诱导成雄性[16-18]; 此外, 有文献报道一些性别相关基因的启动子CpG岛甲基化修饰通过介导时空表达水平影响性别比例[19-22]。但是, 对于甲基化调控性别决定的分子机制尚需更深入的研究。
翘嘴鲌(Culter alburnus Basilewsky)俗称白鱼, 广泛分布于长江流域各水系及附属湖泊, 肉白而细嫩, 味美而不腥, 一贯被视为上等经济鱼类, 在湖泊和水库渔业中占有重要的地位[23]。翘嘴鲌有着明显的性别异型特征, 雌性个体在生长速度和商品规格方面比雄鱼更有优势[24]。因此, 探索性别决定及性腺分化相关的分子调控机制, 进而寻求性别决定基因, 开展全雌翘嘴鲌育种技术, 对于增加经济效益和提升产业体系意义重大。近年来, 我们已经克隆了一些翘嘴鲌性别决定和分化通路中的重要基因, 如Sox9、Dmrt1及Cyp19a[25-27], 并对它们进行了初步的功能分析, 结果表明尽管这些基因在翘嘴鲌雌雄间存在二态性表达特征, 但并不是性别决定主效基因。本研究我们以翘嘴鲌为实验对象, 运用RT-PCR和RACE等克隆手段首次成功鉴定并获得了igf3基因的cDNA全长序列, 随后通过实时荧光定量技术检测了其在不同组织的表达水平。为进一步研究DNA甲基化修饰在该基因性二态性表达特征中的调控作用, 利用重亚硫酸盐测序技术分析了性腺组织的DNA甲基化修饰水平, 这些初步实验结果可为进一步研究igf3基因在翘嘴鲌中的功能及其在性别控制育种中的价值提供参考资料。
1. 材料与方法
1.1 实验材料
本实验使用的性成熟翘嘴鲌(雌雄各3尾)收集于浙江省淡水水产研究所八里店综合试验养殖基地, 鱼活体运回实验室, 在冰浴中解剖鱼体取出肝、心脏、肾、肌肉、脑和雌雄翘嘴鲌的性腺等组织, 液氮冻存, 用于提取基因组DNA和总RNA。
1.2 RNA提取和cDNA合成
本实验采用Trizon法提取总RNA, 各组织样品在Trizon提取试剂中充分裂解, 加入氯仿离心后收集上层清液, 经异丙醇沉淀回收得到Total RNA。选取质量和完整性较好的卵巢RNA为模板, 按照HiFiScript cDNA第一链合成试剂盒(康为 北京)方法合成cDNA第一条链。
1.3 翘嘴鲌igf3编码区的克隆及cDNA末端扩增
根据已知的斑马鱼等物种igf3 cDNA序列信息设计简并引物, 以反转录合成的第一链cDNA为模板, PCR扩增获得翘嘴鲌igf3编码区中间片段。在已知序列区域分别设计正反向引物5′RACE-1、5′RACE-2和3′RACE-1、3′RACE-2, 并参照SMARTerTM RACE (Clontech Japan)试剂盒说明书进行cDNA末端扩增, 最后进行连锁分析获得igf3基因全长序列。
1.4 氨基酸预测、比对及进化树分析
利用JELLYFISH软件分析了翘嘴鲌igf3基因的核苷酸序列及开放阅读框和氨基酸序列的预测; DNAMAN软件对不同物种IGF3氨基酸序列进行了同源性比对; 应用MEGA 5. 0软件的邻接法(Neighbor-joining)法构建了系统进化树, 每个点的计算重复为1000次。
1.5 igf3基因组织表达特征分析
首先利用Primer Express 5.0设计跨内含子的igf3靶基因和ef-1α内参定量引物(表 1), 我们使用的是北京康为世纪生物科技有限公司的UltraSYBR Mixture染料用于实时荧光定量PCR检测。反应条件为: 95℃, 10min, 1个循环; 95℃, 15s, 60℃, 60s, 40个循环。实时定量PCR反应及后续信息都在LightCycler 480 System(Roche 瑞士)上进行。由于定量反应非常敏感, 我们对每个反应设定了3个平行, 最后采用2–ΔΔCt法计算表达量[28]并使用GraphPad Prism 5软件获得直方图。
表 1 用于本实验的引物序列Table 1. Primers used in this study引物名称Primer name 引物序列Sequences (5′—3′) 目的Application igf3-F TGCTGAAGGTGCCCAGCTGGCGGAGT 中间片段扩增 igf3-R CTCCAAATGCTGGAGGTCACATCCA 中间片段扩增 5′RACE-1 CACTGCTCGACGATCCCTTTCCCAC The 1st round 5′RACE 5′RACE-2 CAGGACGCAGTACAGGGAGTAGAGGAC The 2nd round 5′RACE 3′RACE-1 CAGAGGCAAACCTGGAGCAGCCCGTAG The 1st round 3′RACE 3′RACE-2 CGTGGGAAAGGGATCGTCGAGCAGT The 2nd round 3′RACE RT-igf3-F TGCCATCAGACGGAATGCCAAC qRT-PCR RT-igf3-R GCAGAATCAGGACGCAGTACAGG qRT-PCR ef-1α-F ACATGAGGCAGACCGTTGCT qRT-PCR ef-1α-R GGCAGCCTTCTGTGCAGATT qRT-PCR Walking-AS1 CTCTAAGCATCTGAATGTGTCTGGC 启动子扩增 Walking-AS2 TGCTCTTATAGGAGGACCGGGAGG 启动子扩增 igf3-BSP-F ATGGATTTTAATGTTATGTTGTAGG BSP分析 igf3-BSP-R TTATAATTTAATCTCTCTAAAAAACTACTAAC BSP分析 1.6 igf3启动子区域扩增及CpG岛甲基化检测
基于前面扩增获得的igf3 mRNA序列设计了邻近翻译起始位点的两条反向引物Walking-AS1和Walking-AS2, 以翘嘴鲌卵巢基因组DNA为材料, 根据Genome WalkerTM Universal Kit (CloneTech, 日本)试剂盒方法构建基因组文库, 利用特异性引物PCR扩增未知的近端启动子区域。随后对近端启动子序列通过在线软件MethPrimer (http://www.urogene.org/methprimer/)和ALGGEN (http://alggen.lsi.upc.es/)分别进行了CpG岛和转录因子结合位点的预测分析。在线软件MethPrimer预测结果显示有一个符合标准的CpG岛(CG碱基比例>60%且CpG观测值/预测值>0.6)。随后按照CpGenomeTM DNA Modification Kit (Chemicon, USA)试剂盒说明书对翘嘴鲌精巢和卵巢基因组样品(各3尾)进行重亚硫酸氢盐处理, 以处理完成的样品组织为模板, 利用预测获得的甲基化分析引物对igf3-BSP-F和igf3-BSP-R进行甲基化特异性扩增, 最后将产物进行纯化、连接和测序分析。在测序结果中, 甲基化的胞嘧啶不发生变化, 不甲基化的则转变为胸腺嘧啶, 根据是否发生转变便可辨别甲基化修饰模式。
2. 结果
2.1 igf3基因的cDNA全长克隆
本实验通过已经报道的鲤igf3(GenBank 登录号: KT895500)基因序列设计简并引物igf3-F和igf3-R, PCR扩增到长度接近260 bp的电泳条带, 经测序和BLAST同源性分析, 证明其为斑马鱼和鲤igf3的同源片段。随后利用SMARTerTM RACE试剂盒分别进行5′/3′-RACE末端扩增, 最后通过RT-PCR全长序列克隆和连锁分析成功获得了igf3基因的完整cDNA序列。该序列全长901 bp (GenBank登录号: MT418905), 其中包含92 bp的5′端非编码区和203 bp的3′端非编码区, 开放阅读框(ORF) 606 bp, 编码201个氨基酸。序列分析显示, 类似于其他IGF家族成员igf1和igf2, igf3同样存在保守的特征结构域, 主要划分为前体信号肽、B、C、A、D和E区。
2.2 翘嘴鲌IGF3氨基酸序列比对及进化分析
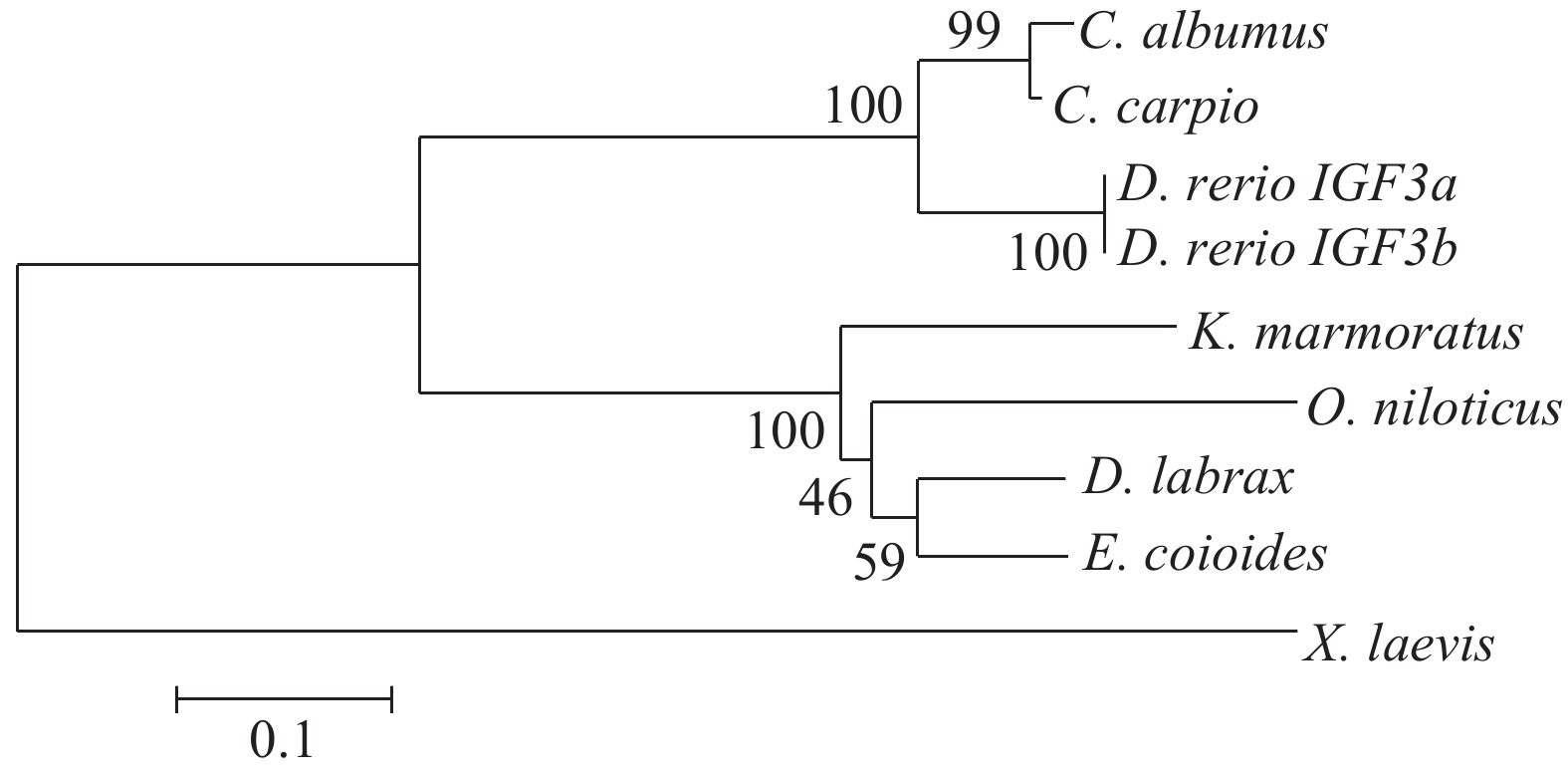
使用JELLYFISH软件对翘嘴鲌igf3核苷酸序列推测出的氨基酸与其他脊椎动物的同源性分析表明, 与鲤(Cyprinus carpio, GenBank登录号: KT895500)的序列同源性最高, 为85.64%; 与斑马鱼(D. rerio, GenBank登录号: ADO16599)次之, 为70.65%; 其次为点带石斑鱼(36.57%, E. coioides, GenBank登录号: AML84199)、尼罗罗非鱼(30.20%, Oreochromis niloticus, GenBank登录号: ABY88870)、海鲈(29.25%, Dicentrarchus labrax, GenBank登录号: AGB51126)、斑纹隐小鳉(25.74%, Kryptolebias marmoratus, GenBank登录号: AGA82753); 和爪蟾(Xenopus laevis, GenBank登录号: NP_001082137)的同源性最低, 为18.93%。采用MEGA 5.0软件的NJ邻接法构建了翘嘴鲌IGF3蛋白与其他7个物种的系统进化树(图 1)。结果显示翘嘴鲌与鲤发生聚类, 较其他物种具有最接近的亲缘关系, 所有鱼类聚为一支, 爪蟾单独构成一支。
2.3 翘嘴鲌igf3表达水平分析
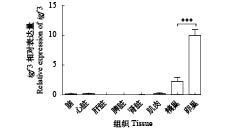
以ef-1α为内参基因, 采用qRT-PCR方法对igf3基因mRNA在翘嘴鲌各组织的表达丰度进行了分析。结果显示igf3基因在翘嘴鲌不同组织中的表达丰度差异明显, 在卵巢中表达量最高, 其次是精巢组织, 而在脑、心脏、脾脏、肝脏、肌肉和肾脏中表达丰度极低(图 2)。这表明igf3基因在性腺中的表达水平显著高于其他组织, 提示其在性腺形成或功能维持方面具有重要作用。
2.4 翘嘴鲌igf3启动子区域CpG岛甲基化分析
为了解翘嘴鲌的卵巢和精巢中igf3基因启动子CpG岛甲基化程度, 我们对该基因近端启动子序列进行了扩增和CpG岛预测。结果表明该基因启动子区域存在一段包含8个CG位点的CpG岛(图 3a)。经重亚硫酸氢盐处理翘嘴鲌精巢和卵巢基因组, PCR检测结果显示在卵巢中的10个随机挑选克隆所有CG位点几乎不发生甲基化修饰, 相反精巢中高度甲基化(只有一个克隆的CG位点没有发生甲基化), 两个性腺组织甲基化修饰水平差异显著(图 3b和3c)。这个结果表明igf3在性腺组织中的表达丰度与DNA甲基化修饰程度正好呈负相关, 提示翘嘴鲌性别二态性表达特征可能受其启动子区域CpG岛甲基化修饰的调控。
![]() 图 3 翘嘴鲌igf3基因启动子CpG岛甲基化分析a. igf3启动子区域CpG岛及转录因子结合位点预测。CG位点用粗体标注, 上面的数字表示其在启动子区域的所处位置, 灰色背景区域代表各个转录因子结合位点; b、c. 分别表示卵巢和精巢基因组igf3启动子重亚硫酸盐测序结果。实心圆圈代表甲基化的CG位点、空心圆圈代表非甲基化的CG位点。每一行表示一个测序克隆Figure 3. CpGs DNA methylation of igf3 in C. alburnusa. The predicted CpG sites and transcription factors in the proximal promoter of igf3. CpG dinucleotides are shown in bold background, and numbers indicate the location of the CG site in promoter region. The gray background regions represent different transcription factor binding sites; b, c. Bisulfte sequencing results of the igf3 promoter CpG island in the genomes of testis and ovary, respectively. Each line represents an examined clone. Open and filled circles indicate unmethylated or methylated positions
图 3 翘嘴鲌igf3基因启动子CpG岛甲基化分析a. igf3启动子区域CpG岛及转录因子结合位点预测。CG位点用粗体标注, 上面的数字表示其在启动子区域的所处位置, 灰色背景区域代表各个转录因子结合位点; b、c. 分别表示卵巢和精巢基因组igf3启动子重亚硫酸盐测序结果。实心圆圈代表甲基化的CG位点、空心圆圈代表非甲基化的CG位点。每一行表示一个测序克隆Figure 3. CpGs DNA methylation of igf3 in C. alburnusa. The predicted CpG sites and transcription factors in the proximal promoter of igf3. CpG dinucleotides are shown in bold background, and numbers indicate the location of the CG site in promoter region. The gray background regions represent different transcription factor binding sites; b, c. Bisulfte sequencing results of the igf3 promoter CpG island in the genomes of testis and ovary, respectively. Each line represents an examined clone. Open and filled circles indicate unmethylated or methylated positions3. 讨论
鱼类拥有所有脊椎动物都有可能出现的性别决定类型, 因此研究其性别决定和性别分化具有重要的学术价值。更为重要的是, 大多数鱼类在生长过程中存在明显的性别二态性, 即雌雄个体的生长速率、个头大小差异显著, 通过性别调控发展单性养殖技术有着较高的经济价值[29]。已有研究表明IGFs家族除对脊椎动物的生长发育方面具有重要调控作用外, 在性别决定与分化中的作用也受到广泛关注[30]。近年来, 在硬骨鱼中发现一种特有的新型IGF因子(igf3), 且仅出现在精巢和卵巢中的间质细胞[31], 因此其在性腺发育中的作用受到了广泛关注。到目前为止, 已在多个鱼类物种中分离鉴定到igf3基因, 包括斑马鱼、罗非鱼、斜带石斑鱼、双棘黄姑鱼、鲤、虹鳟(Oncorhynchus mykiss)[31]和雀鲷(Chrysiptera cyanea)[32]并进行了一些初步的表达水平和功能机制分析。
3.1 翘嘴鲌igf3的克隆鉴定和保守性分析
本研究报道了翘嘴鲌igf3基因全长cDNA序列, 该基因全长901 bp, 包含开放阅读框606 bp, 92 bp的5′端非编码区和203 bp的3′端非编码区, 编码201个氨基酸。蛋白质结构分析显示翘嘴鲌IGF3同样存在IGF家族特有的典型结构域, 主要划分为前体信号肽、B、C、A、D和E区, 这与罗非鱼、斑马鱼和鲤鱼中的结构较为一致[9, 10, 14]。多重氨基酸序列结果显示所有鱼类物种的IGF3蛋白在保守结构域区域相似度较高, 表明这些保守结构域对于IGF家族发挥功能作用是必需的[12]。根据系统进化树结果, 选择分析的鱼类物种都聚为一支, 这一结果表明IGF3的系统进化关系与物种的分类地位保持一致。此外, 我们还发现igf3基因组启动子区域存在多个与性别相关的转录因子结合位点, 如SRY、Sox2和HMG等, 这些数据有力地证明igf3作为下游基因可能参与翘嘴鲌的性别决定与分化过程。
3.2 翘嘴鲌igf3基因的功能研究
目前发表的研究数据表明igf3在硬骨鱼类性腺中的表达水平都要远高于其他组织, 暗示其在性腺中具有重要的作用[9, 10, 12—14]。翘嘴鲌igf3基因在成体各组织的qRT-PCR结果显示: 该基因主要在卵巢中表达, 其次在精巢中有少量表达, 而其他组织基本无法检测到igf3的表达, 且卵巢中的表达水平显著高于其他组织(P<0.001)。翘嘴鲌成体组织的表达模式推测该基因可能参与成体卵巢的功能维持, 由于igf3基因在精巢中也有少量表达, 提示其功能不仅限于卵巢方面的作用, 对于2个不同性腺组织的形成可能都具有重要的功能。在罗非鱼中的研究表明igf3参与调控性别分化相关基因(cyp19a1a、foxl2和dmrt1)的表达, 同时igf3的表达也受到这些转录因子和雌激素的调控[33]。
在研究鱼类等脊椎动物性别发育调控时会发现许多性别相关基因是雌性或雄性相关基因, 其表达模式显示了明显的性别二态性[34]。本实验对翘嘴鲌性腺组织qRT-PCR的检测结果显示, 卵巢表达量约为精巢的3倍, 说明该基因的表达呈显著的性别二态性。为了解涉及性二态性表达特征的调控机制, 我们对性腺组织的igf3基因启动子区域进行了甲基化分析, 结果表明基因表达水平与DNA甲基化修饰呈负相关关系。在其他鱼类物种中, 如牙鲆(Paralichthys olivaceus)、斑马鱼和黄鳝(Monopterus albus)等脊椎动物, 一些性别调控基因(cyp19a、cyp17和dmrt1)也被发现有两性性腺甲基化水平和基因表达的差异[18, 35]。已知CpG岛所在启动子区域富含转录因子结合位点, igf3在精巢中的高度甲基化可能阻碍了一些转录因子的结合及转录复合物的形成, 进而抑制了该基因的表达, 至于具体的阻碍机制仍需进一步的研究。
本研究基于RACE方法成功克隆了翘嘴鲌igf3 cDNA序列, 并对其蛋白质结构、氨基酸序列同源性、组织表达模式及启动子甲基化修饰水平进行了系统的检测分析, 为进一步揭示igf3对于翘嘴鲌性腺发育的作用奠定了研究基础。但igf3在性别调控和性腺发育中如何发挥作用及表观遗传修饰的具体调控机制仍未可知, 为此后续实验应该围绕如下两方面进行深入研究: (1)通过CRISPR/Cas9基因编辑技术建立功能基因敲除模型, 研究各个基因间的相互作用, 最终阐明翘嘴鲌性别决定与分化过程的调控网络; (2)挖掘igf3潜在的转录因子, 分析其在性别决定与分化关键时期的基因表达和甲基化动态水平的检测分析, 设计体外实验研究转录因子对igf3基因的调控关系。
-
图 3 翘嘴鲌igf3基因启动子CpG岛甲基化分析
a. igf3启动子区域CpG岛及转录因子结合位点预测。CG位点用粗体标注, 上面的数字表示其在启动子区域的所处位置, 灰色背景区域代表各个转录因子结合位点; b、c. 分别表示卵巢和精巢基因组igf3启动子重亚硫酸盐测序结果。实心圆圈代表甲基化的CG位点、空心圆圈代表非甲基化的CG位点。每一行表示一个测序克隆
Figure 3. CpGs DNA methylation of igf3 in C. alburnus
a. The predicted CpG sites and transcription factors in the proximal promoter of igf3. CpG dinucleotides are shown in bold background, and numbers indicate the location of the CG site in promoter region. The gray background regions represent different transcription factor binding sites; b, c. Bisulfte sequencing results of the igf3 promoter CpG island in the genomes of testis and ovary, respectively. Each line represents an examined clone. Open and filled circles indicate unmethylated or methylated positions
表 1 用于本实验的引物序列
Table 1 Primers used in this study
引物名称Primer name 引物序列Sequences (5′—3′) 目的Application igf3-F TGCTGAAGGTGCCCAGCTGGCGGAGT 中间片段扩增 igf3-R CTCCAAATGCTGGAGGTCACATCCA 中间片段扩增 5′RACE-1 CACTGCTCGACGATCCCTTTCCCAC The 1st round 5′RACE 5′RACE-2 CAGGACGCAGTACAGGGAGTAGAGGAC The 2nd round 5′RACE 3′RACE-1 CAGAGGCAAACCTGGAGCAGCCCGTAG The 1st round 3′RACE 3′RACE-2 CGTGGGAAAGGGATCGTCGAGCAGT The 2nd round 3′RACE RT-igf3-F TGCCATCAGACGGAATGCCAAC qRT-PCR RT-igf3-R GCAGAATCAGGACGCAGTACAGG qRT-PCR ef-1α-F ACATGAGGCAGACCGTTGCT qRT-PCR ef-1α-R GGCAGCCTTCTGTGCAGATT qRT-PCR Walking-AS1 CTCTAAGCATCTGAATGTGTCTGGC 启动子扩增 Walking-AS2 TGCTCTTATAGGAGGACCGGGAGG 启动子扩增 igf3-BSP-F ATGGATTTTAATGTTATGTTGTAGG BSP分析 igf3-BSP-R TTATAATTTAATCTCTCTAAAAAACTACTAAC BSP分析 -
[1] Mei J, Gui J F. Genetic basis and biotechnological manipulation of sexual dimorphism and sex determination in fish [J]. Science China Life Sciences, 2015, 58(2): 124-136. doi: 10.1007/s11427-014-4797-9
[2] Piferrer F, Ribas L, Díaz N. Genomic approaches to study genetic and environmental influences on fish sex determination and differentiation [J]. Marine Biotechnology, 2012, 14(5): 591-604. doi: 10.1007/s10126-012-9445-4
[3] Li X Y, Gui J F. Diverse and variable sex determination mechanisms in vertebrates [J]. Science China Life Sciences, 2018, 61(12): 1503-1514. doi: 10.1007/s11427-018-9415-7
[4] Duan C M. Insulin-like growth factor signaling in fish [J]. International Review of Cytology, 2005(243): 215-285.
[5] Stewart C E, Rotwein P. Growth, differentiation, and survival: multiple physiological functions for insulin-like growth factors [J]. Physiological Reviews, 1996, 76(4): 1005-1026. doi: 10.1152/physrev.1996.76.4.1005
[6] Werner H, Karnieli E, Leroith R D. Wild-type and mutant p53 differentially regulate transcription of the insulin-like growth factor I receptor gene [J]. Proceedings of the National Academy of Sciences of the United States of America, 1996, 93(16): 8318-8323. doi: 10.1073/pnas.93.16.8318
[7] Kagawa H, Moriyama S, Kawauchi H. Immunocytochemical localization of IGF-I in the ovary of the red seabream, Pagrus major [J]. General Comparative Endocrinology, 1995, 99(3): 307-315. doi: 10.1006/gcen.1995.1114
[8] Berishvili G, Helena D’Cotta, Baroiller J F, et al. Differential expression of IGF-I mRNA and peptide in the male and female gonad during early development of a bony fish, the tilapia Oreochromis niloticus [J]. General & Comparative Endocrinology, 2006, 146(3): 204-210.
[9] Nelson S N, Kraak G V D. The role of the insulin-like growth factor (IGF) system in zebrafish (Danio rerio) ovarian development [J]. General Comparative Endocrinology, 2010, 168(1): 103-110. doi: 10.1016/j.ygcen.2010.04.021
[10] Wang D S, Jiao B, Hu C, et al. Discovery of a gonad-specific IGF subtype in teleost [J]. Biochemical & Biophysical Research Communications, 2008, 367(2): 1-341.
[11] Zou S, Kamei H, Modi Z, Duan C. Zebrafish IGF genes: gene duplication, conservation and divergence, and novel roles in midline and notochord development [J]. PLoS One, 2009(4): e7026.
[12] Yang H, Chen H, Zhao H, et al. Molecular cloning of the insulin-like growth factor 3 and difference in the expression of igf genes in orange-spotted grouper (Epinephelus coioides) [J]. Comparative Biochemistry & Physiology Part B Biochemistry & Molecular Biology, 2015, 186(2015): 68-75.
[13] 林权卓, 陈奕彬, 胡娟, 等. 双棘黄姑鱼IGF3基因克隆及表达模式分析 [J]. 南方水产科学, 2016, 12(1): 50-58. doi: 10.3969/j.issn.2095-0780.2016.01.008 Lin Q Z, Chen Y B, Hu J, et al. IGF3 gene cloning and expression pattern of Protonibea diacanthus [J]. South China Fisheries Science, 2016, 12(1): 50-58. doi: 10.3969/j.issn.2095-0780.2016.01.008
[14] Song F, Wang L, Zhu W, et al. A novel igf3 gene in common carp (Cyprinus carpio): evidence for its role in regulating gonadal development [J]. PLoS One, 2016, 11(12): e0168874. doi: 10.1371/journal.pone.0168874
[15] Li X Y, Gui J F. An epigenetic regulatory switch controlling temperature-dependent sex determination in vertebrates [J]. Science China Life Sciences, 2018, 61(8): 996-998. doi: 10.1007/s11427-018-9314-3
[16] Navarro-Martín L, Viñas J, Ribas L, et al. DNA methylation of the gonadal aromatase (cyp19a) promoter is involved in temperature-dependent sex ratio shifts in the European sea bass [J]. PLoS Genetics, 2011, 7(12): e1002447. doi: 10.1371/journal.pgen.1002447
[17] Zhang Y, Zhang S, Liu Z, et al. Epigenetic modifications during sex change repress gonadotropin stimulation of cyp19a1a in a teleost ricefield eel (Monopterus albus) [J]. Endocrinology, 2013, 154(8): 2881-2890. doi: 10.1210/en.2012-2220
[18] Bai J, Gong W, Wang C, et al. Dynamic methylation pattern of cyp19a1a core promoter during zebrafish ovarian folliculogenesis [J]. Fish Physiology and Biochemistry, 2016, 42(3): 947-954. doi: 10.1007/s10695-015-0187-x
[19] Wen A Y, You F, Sun P, et al. CpG methylation of dmrt1 and cyp19a promoters in relation to their sexual dimorphic expression in the Japanese flounder Paralichthys olivaceus [J]. Journal of Fish Biology, 2014, 84(1): 193-205. doi: 10.1111/jfb.12277
[20] Nishino K, Hattori N, Tanaka S, et al. DNA methylation-mediated control of sry gene expression in mouse gonadal development [J]. Journal of Biological Chemistry, 2004, 279(21): 22306-22313. doi: 10.1074/jbc.M309513200
[21] Mamta P, Puja S, Alka S, et al. Methylation of the sox9 and oct4 promoters and its correlation with gene expression during testicular development in the laboratory mouse [J]. Genetics and Molecular Biology, 2016, 39(3): 452-458. doi: 10.1590/1678-4685-GMB-2015-0172
[22] Strömqvist M, Tooke N, Brunström B. DNA methylation levels in the 5′ flanking region of the vitellogenin I gene in liver and brain of adult zebrafish (Danio rerio)-Sex and tissue differences and effects of 17a-ethinylestradiol exposure [J]. Aquatic Toxicology, 2010, 98(3): 275-281. doi: 10.1016/j.aquatox.2010.02.023
[23] 顾志敏, 朱俊杰, 贾永义, 等. 太湖翘嘴红鲌胚胎发育及胚后发育观察 [J]. 中国水产科学, 2008, 15(2): 204-214. doi: 10.3321/j.issn:1005-8737.2008.02.003 Gu Z M, Zhu J J, Jia Y Y, et al. Research on embryonic and postembryonic development of Erythroculter ilishaeformis Bleeker of Taihu Lake [J]. Journal of Fishery Sciences of China, 2008, 15(2): 204-214. doi: 10.3321/j.issn:1005-8737.2008.02.003
[24] 刘祥芳, 郑建波, 贾永义, 等. 翘嘴红鲌雌雄基因组差异及太湖野生群体遗传多样性现状的AFLP分析 [J]. 水生生物学报, 2017, 41(6): 1200-1206. doi: 10.7541/2017.149 Liu X F, Zheng J B, Jia Y Y, et al. AFLP analysis on genomic sexual dimorphism of ertthroculture ilishaeformis and current genetic diversity of the Taihu strain [J]. Acta Hydrobiologica Sinica, 2017, 41(6): 1200-1206. doi: 10.7541/2017.149
[25] 贾永义, 郑建波, 顾志敏, 等. 翘嘴鲌Sox9基因的克隆及CpG岛甲基化与基因表达的关系 [J]. 水生生物学报, 2019, 43(3): 473-478. doi: 10.7541/2019.058 Jia Y Y, Zheng J B, Gu Z M, et al. The relationship of Sox9 expression and its CpG island methylation in Culter alburnus [J]. Acta Hydrobiologica Sinica, 2019, 43(3): 473-478. doi: 10.7541/2019.058
[26] Jia Y, Zheng J, Chi M, et al. Molecular identification of dmrt1 and its promoter CpG methylation in correlation with gene expression during gonad development in Culter alburnus [J]. Fish Physiology & Biochemistry, 2018, 45(1): 245-252.
[27] Zheng J, Jia Y, Li F, et al. Molecular characterization and expression analysis of cyp19a gene in Culter alburnus [J]. Fisheries Science, 2019, 85(3): 1-10.
[28] Livak K J, Schmittgen T D. Analysis of relative gene expression data using real-time quantitative PCR and the 2(-Delta Delta C(T)) Method [J]. Methods (San Diego, Calif.), 2001, 25(4): 402—408.
[29] Bonduriansky R, Chenoweth S F. Intralocus sexual conflict [J]. Trends in Ecology & Evolution, 2009(24): 280-288.
[30] Lu C X, Lam H N, Menon R K. New members of the insulin family: regulators of metabolism, growth and now. Reproduction [J]. Pediatric Research, 2005, 57(2): 70R.
[31] Middleton M A, Larsen D A, Dickey J T, et al. Evaluation of endocrine and transcriptomic markers of male maturation in winter-run steelhead trout (Oncorhynchus mykiss) [J]. General and Comparative Endocrinology, 2019(281): 30-40.
[32] Rizky D, Mahardini A, Byun J, et al. Molecular cloning of insulin-like growth factor 3 (igf3) and its expression in the tissues of a female damselfish, Chrysiptera cyanea, in relation to seasonal and food-manipulated reproduction [J]. General and Comparative Endocrinology, 2020(295): 113479.
[33] Li M, Wu F, Gu Y, et al. Insulin-like growth factor 3 regulates expression of genes encoding steroidogenic enzymes and key transcription factors in the Nile tilapia gonad [J]. Biology of Reproduction, 2012, 86(5): 163-172.
[34] Alam M A, Kobayashi Y, Horiguchi R, et al. Molecular cloning and quantitative expression of sexually dimorphic markers Dmrt1 and Foxl2 during female-to-male sex change in Epinephelus merra [J]. General and Comparative Endocrinology, 2008, 157(1): 75-85. doi: 10.1016/j.ygcen.2008.03.018
[35] Ding Y, He F, Wen H, et al. DNA methylation status of cyp17-II gene correlated with its expression pattern and reproductive endocrinology during ovarian development stages of Japanese flounder (Paralichthys olivaceus) [J]. Gene, 2013, 527(1): 82-88. doi: 10.1016/j.gene.2013.05.037
-
期刊类型引用(1)
1. 张家荣,秦宏宇,谢婷,张效宇,李飞霞,吕俊贤,贾玉东. 大菱鲆类胰岛素生长因子3基因的克隆和表达分析. 渔业科学进展. 2024(02): 220-232 .  百度学术
百度学术
其他类型引用(0)



 下载:
下载: