ISOLATION OF MICROSATELLITE LOCI AND GENETIC DIVERSITY ANALYSIS OF SINOGASTROMYZON SICHANGENSIS
-
摘要: 采用高通量测序法对西昌华吸鳅(Sinogastromyzon sichangensis)基因组进行随机测序并筛选出符合条件的微卫星位点, 设计可用于PCR扩增的引物, 筛选出29对具有多态性的引物, 平均等位基因数为14.5, 观测杂合度(Ho)和期望杂合度(He)分别为0.620和0.882, 多态信息含量(PIC)为0.859。选取其中多态性较高的20对引物在赤水河及其支流的4个地理种群中进行扩增, 分析不同地理种群的遗传多样性和种群分化情况。结果表明, 赤水镇种群观测杂合度最高(0.669), 茅台镇种群观测杂合度最低(0.520); 习水河多态信息含量最高(0.868), 茅台镇种群多态信息含量最低(0.841)。赤水河干流的几个种群未出现显著分化, 而习水河种群与其他3个种群的遗传分化程度较高。AMOVA分析显示遗传变异主要发生在群体内, 群体间遗传变异仅占3.33%, 群体内遗传变异占96.67%。种群遗传结构分析表明, 赤水河干流整体遗传背景趋于一致, 而习水河种群则单独聚为一个亚类群。研究为西昌华吸鳅的资源保护和种群遗传学研究提供了基础资料。Abstract: Sinogastromyzon sichangensis is a small-size fish endemic to the upper Yangtze River mainly distributed in main stream and tributaries. Twenty-nine polymorphic microsatellite loci of the S. sichangensis were isolated by next-generation sequencing techniques. Four wild populations in Chishui River were amplified by 20 loci with mean alleles 14.5. The mean observed (Ho) and expected (He) heterozygosity were 0.620 and 0.882, respectively and the mean polymorphic information content (PIC) was 0.859. The Ho ranged from 0.520 (Maotai Town) to 0.669 (Chishui Town) and PIC ranged from 0.841 (Maotai Town) to 0.868 (Xishui River). The Fst value and analysis of population structure revealed a genetic differentiation between populations from Xishui River and the main stream of Chishui River. AMOVA showed that the genetic variation was 3.33% among populations while it was 96.67% within populations. These novel loci could use to investigate the population genetics and biological resource conservation strategy in S. sichangensis.
-
西昌华吸鳅(Sinogastromyzon sichangensis)隶属于鲤形目(Cypriniformes), 爬鳅科(Balitoridae), 华吸鳅属(Sinogastromyzon), 是长江上游特有的一种小型鱼类, 主要分布于长江上游干流及部分支流[1]。赤水河为长江右岸一级支流, 流经滇、川、黔, 于四川省合江县汇入长江, 全长466 km。西昌华吸鳅是赤水河上、中游及部分支流的常见种[2], 喜急流环境, 利用腹鳍愈合成的吸盘栖息于溪流的砂石上[3]。目前, 关于西昌华吸鳅的研究报道较少, 早期多见于生物学研究[4-6]及保护生物学研究[7-10]。近年来, 随着分子生物学的发展, 相关类群的系统发育研究逐渐展开[11-13], 李小娟[14]基于线粒体Cyt b及核基因(EGR2、BIRBP、Zic1)对华吸鳅属鱼类物种分化进行了研究。但是西昌华吸鳅的种群遗传学研究仍然缺乏。
微卫星DNA标记由于具有共显性、高度遗传多态性和等位基因分型难度低等优点, 得到了广泛的应用, 而高多态性的微卫星位点也已成为种群遗传学研究的普遍选择[15]。本研究利用高通量测序技术共筛选出西昌华吸鳅29对具有多态性的微卫星引物, 并利用其中20对引物对赤水河4个地理种群的遗传多样性、种群分化及遗传结构进行分析, 为长江上游特有鱼类的保护积累资料。
1. 材料与方法
1.1 样品采集与总DNA提取
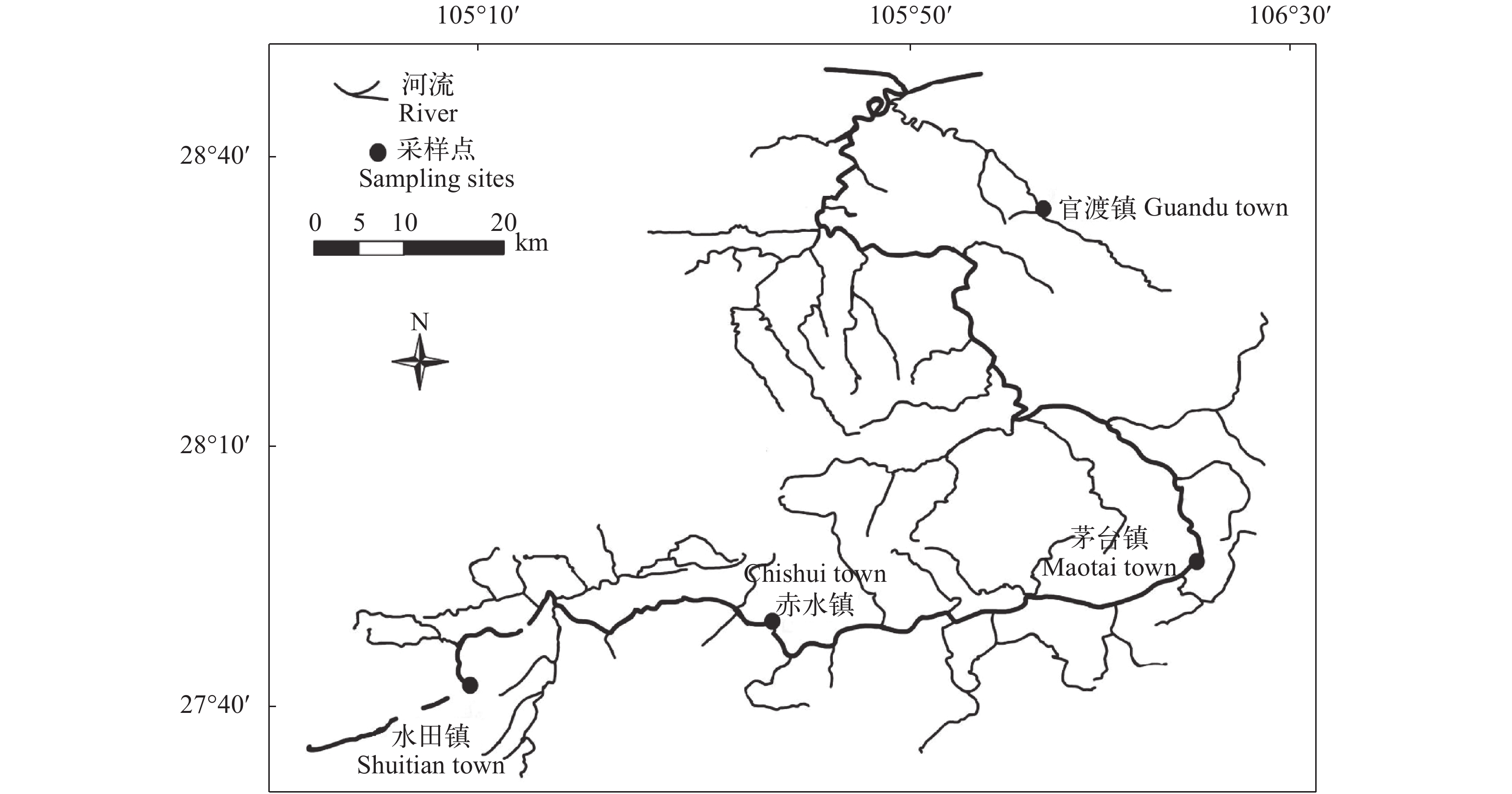
2016年5月至9月分别于赤水河源头云南水田镇(ST), 上游四川赤水镇(CSZ), 中游贵州茅台镇(MT)及赤水河支流习水河官渡镇(XS)河段采集西昌华吸鳅样本(图 1), 每个地点各取30尾西昌华吸鳅剪取背部肌肉固定于95%乙醇溶液, 保存于中国科学院水生生物研究所淡水鱼类博物馆。基因组DNA的提取采用高盐抽提法[16], 并用1.0%琼脂糖凝胶电泳检测DNA提取质量, 置于–20℃保存备用。
1.2 高通量测序、微卫星位点挖掘及筛选
使用Illumina Miseq测序仪对西昌华吸鳅一个个体的基因组DNA进行全基因组测序, 过滤掉接头、低质量序列后先进行基因组组装, 之后通过MISA软件(http://pgrc.ipk-gatersleben.de/misa/)对微卫星位点进行搜索。选取重复类型三碱基或四碱基, 重复次数大于5且长度在70—500 bp的片段进行引物开发, 引物设计在NCBI的Primer-BLAST网页(https://www.ncbi.nlm.nih.gov/tools/primer-blast/)在线完成[17]。
随机选取8尾西昌华吸鳅个体的基因组DNA尾模板对设计的引物进行筛选并优化反应条件。PCR反应体系包括100 ng模板DNA, 10 μL 2×Master Mix (TSKINGKE), 上下游引物各1 μL并用灭菌水补充至20 μL总体系。PCR反应程序为: 95℃预变性5min; 95℃变性30s, Tm退火30s (表 1), 72℃延伸45s, 以上程序30个循环重复; 最后72℃延伸5min。反应产物采用30%非变性聚丙烯酰胺凝胶电泳检测, 经Ultra GelRed (Vazyme) 水溶液浸染后, 在GeneSnap (Syngene) 紫外成像系统下拍照保存。
表 1 西昌华吸鳅微卫星位点及PCR引物信息Table 1. Information of polymorphic microsatellite markers of S. sichangensis位点Loci 引物序列Primer sequence (5′-3′) 重复单元
Repeat motif片段大小
Size range (bp)退火温度Tm (℃) SS010 TGACTGATGCATGACGGACT GCAAAATGTGCTGCAAGACG (TGTA)22 223—310 55 SS017 CGTGATGAAAAACTGCTGCG TCACTCGTTCGCTCATTCACT (TTCA)11 97—140 56 SS018 GCACCACCCATCTGTTGTTG AATCCCACAGCTTTTTCACACA (ACAT)11 128—171 54 SS025 GTCCAAAATATCATTTAGCCCAGCA AAGGTGGATGGAGGGAAATCTG (CTGT)21 74—157 53 SS030 ATCCTGAGCTGTCGCCTTAC CAGCGTGCGCCCTAGTTTTA (AACA)10 263—302 60 SS036 TGCAGAATGAGGTGGACACA ATCAAACTCACAGCTAGGCAG (TGTT)9 248—283 55 SS042 GTTTGGCACAGATCTCGGTT AAAGTCATAAATCCTGGACAGTT (TTCT)28 164—275 53 SS045 CACCCGTCTCACAACATGAC ATGCAGCTTTGGCATTGCAC (GAT)14 161—202 55 SS050 CACGTGTGATCGCAGACAAA GGGAAGGCTTGCTTTACCTTCT (ATA)10 84—113 58 SS051 AGGTTTGGGATAAGTTCAGGGAC TAACAGATTCCATCCAGGGCT (ACA)10 252—281 55 SS053 AGCTCTTAAATAGGCCAAGTGTT AAGGTGGTGGTGTTAAGGTGT (GATA)23 134—225 55 SS055 AAAACCCTACACACCCTGCTT GGCTGCTCATGCAAACCAAT (GATA)22 109—196 55 SS061 TTAAACTGACCGGCGAGCAA TGTATGTGCAGGATGAGAGCG (TCC)11 119—151 56 SS063 GTGCGCCTCGTTGATCTTCT AAAAACAGCGTGACGTGGATG (GAA)11 151—183 55 SS064 CTATATATAAGCGACGCCGAGC ACTGCTCTTTACGTCCTCTGG (AGA)26 105—182 57 SS066 TTGCGGCTGTACGCAGAAT CGGGATGCGGATGACTACAG (CAA)12 73—108 56 SS073 TGATTGCCCAGGTGTGTGTT ACACCTGTTCAGTGAATCATCC (AAT)11 195—227 51 SS075 GCAGAAAGGTCAGTGTAAGGGA CCACAGACTGCACTTGCACA (AAT)11 181—213 54 SS080 TGTTAATCTGCTGCCGTGGG GGAGCGGGTTAAGAAGACACT (GCGT)9 174—209 55 SS083 GCTGATACCTGTTTAGCTGTTGC TCCACTCCGTTAGATGAGGTC (GATA)44 125—300 57 SS090 GCAGTAGGCAATTTGCAATAAGT ATCCACACACACACGACTGG (TATC)41 95—258 53 SS091 GACATTCCCTGATGCGGACA TTGCCACAGTCAAAGTGGGT (CTGT)10 124—163 58 SS108 GTTTGCGCTTTCTGTGCTGA AAGCAACGTCTTTCGGATGC (GACA)9 205—240 55 SS109 TCGTTGTCGTGTAAACAGCC CCGTACAGGTGCATGTGACT (TAT)10 73—102 58 SS110 GCAGAATGTGCACCTTGGAAA ATTGCTGCACATTAGAAGTGG (ATAC)11 128—171 53 SS112 ACTTTCATGGCATGTGGTGTG TCACACGAAGTGAACTGCCA (ATCT)12 83—130 51 SS116 GTCTCTGCTGAGGCAATTCG CGCCCATCACTACCGATAACT (TGA)14 204—245 55 SS129 TGTGCTGGACAAACATGCTG AGGTCAAAGGTTAGTGTTGGGT (TCA)20 211—258 53 SS144 CAGCACAAGTGGAAGAACACTTT AAAGACCAGTTTAATGGGAGCA (ATAG)12 79—126 54 注: 全部位点信息已上传至GenBank, 登录号为MH745718—MH745746Note: Information of all loci was submitted to GenBank (Accession numbers: MH745718—MH745746) 1.3 种群扩增与读带
选取20对多态性引物, 对赤水河4个不同地理种群的西昌华吸鳅进行扩增, 反应体系和程序同上, 利用pBR322DNA/MspⅠ和pUC18DNA/MspⅠ (Tiangen) 为参照以确定不同位点等位基因大小。利用GeneSnap凝胶成像系统自动标记扩增的PCR片段并辅以人工校正, 与pBR及pUC进行比较, 最后读取不同等位基因大小。
1.4 数据处理与分析
原始数据通过CONVERT 1.31软件转化为各软件所需格式[18]。利用MICRO-CHECKER软件检查有无出现等位基因缺失、无效等位基因 (Null allele)或者由于结巴带(Shutter)引起的错配等情况[19]。通过GENEPOP检验微卫星位点是否符合哈迪温伯格平衡[20]。利用Cervus 3.03软件计算几个不同地理种群西昌华吸鳅的等位基因数(Number of alleles, Na)、观测杂合度(Observed heterozygosity, Ho)和期望杂合度(Expected heterozygosity, He)、多态信息含量(Polymorphic information content, PIC)[21]。利用Arlequin3.5软件估算几个种群的遗传分化指数(Fst)并进行分子变异分析方法(AMOVA)分析[22]。通过Structure软件对西昌华吸鳅种群结构进行分析[23, 24]。
2. 结果
2.1 微卫星标记筛选
高通量测序共获得34401条存在微卫星位点的序列。在检出的微卫星序列中, 二核苷酸占优势, 占全部微卫星序列的51.50%; 三核苷酸次之, 占总序列的34.54%; 其次是四核苷酸, 为6.46%; 五、六核苷酸最少, 合计占总序列的7.50%。根据微卫星位点筛选要求和引物设计原则, 共设计144对引物, 其中52对引物成功扩增, 但只有29对引物显示了较高的多态性, 引物基本信息详见表 1。
2.2 种群遗传多样性及遗传分化
选取20对多态性较高的引物对西昌华吸鳅4个地理种群进行扩增, 种群遗传多样性结果如表 2所示。西昌华吸鳅四个地理种群的等位基因数在7—28; 赤水镇种群平均观测杂合度最高, 为0.669; 水田镇种群的期望杂合度最高, 为0.890; 茅台镇种群观测杂合度和期望杂合度最低, 分别为0.520和0.867; 习水河种群平均多态信息含量最高为0.868。4个种群分别有2到8个位点偏离哈迪温伯格平衡, 所有地理种群西昌华吸鳅的平均多态信息含量均大于0.86, 表明西昌华吸鳅几个种群的遗传多样性处于较高水平。
表 2 西昌华吸鳅4个种群微卫星标记的遗传学特征Table 2. Characteristics of the 20 microsatellite loci in 4 populations of S. sichangensis种群
Population位点Loci Mean SS10 SS17 SS25 SS36 SS45 SS53 SS61 SS63 SS73 SS75 SS80 SS90 SS108 SS110 SS112 SS116 SS129 SS144 SS109 SS51 ST Na 23 17 21 10 10 17 9 13 13 15 23 19 8 13 22 13 8 17 17 10 14.9 Ho 0.75 0.55 0.80 0.45 0.62 0.48 0.47 0.53 0.57 0.83 0.35 0.77 0.76 0.45 0.80 0.90 0.69 0.90 0.62 0.69 0.649 He 0.95 0.93 0.94 0.86 0.83 0.92 0.83 0.86 0.87 0.89 0.95 0.94 0.82 0.89 0.95 0.91 0.81 0.94 0.92 0.78 0.890 PIC 0.93 0.91 0.93 0.84** 0.80 0.90 0.80* 0.84 0.85 0.86 0.93 0.92 0.79 0.86 0.93 0.89 0.78 0.93 0.90 0.74 0.867 CSZ Na 28 16 19 11 11 21 7 11 9 13 22 15 10 15 19 12 11 14 19 7 14.5 Ho 0.80 0.77 0.86 0.66 0.83 0.45 0.32 0.70 0.73 0.80 0.63 0.90 0.90 0.43 0.87 0.70 0.33 0.53 0.69 0.48 0.669 He 0.95 0.92 0.92 0.86 0.85 0.95 0.78 0.89 0.88 0.89 0.95 0.91 0.85 0.88 0.94 0.89 0.83 0.89 0.93 0.78 0.887 PIC 0.94 0.90 0.90 0.83 0.83 0.93 0.74* 0.87* 0.76 0.87 0.94 0.89 0.83 0.86* 0.93 0.87* 0.80** 0.87 0.91 0.74** 0.861 MT Na 24 18 18 10 9 21 8 10 15 16 13 20 9 17 19 14 9 23 12 7 14.6 Ho 0.87 0.45 0.59 0.64 0.37 0.48 0.47 0.40 0.50 0.37 0.20 0.87 0.53 0.40 0.87 0.73 0.53 0.67 0.10 0.35 0.520 He 0.95 0.90 0.93 0.81 0.77 0.95 0.82 0.79 0.89 0.88 0.70 0.95 0.85 0.92 0.94 0.89 0.84 0.94 0.89 0.72 0.867 PIC 0.93 0.88** 0.91 0.78 0.74* 0.94 0.78 0.75** 0.87 0.86** 0.68** 0.93 0.82 0.90 0.92 0.86 0.80* 0.92 0.87** 0.68** 0.841 XS Na 26 16 19 13 10 20 10 9 12 11 15 19 10 11 20 12 8 19 15 8 14.1 Ho 0.70 0.73 0.57 0.70 0.67 0.33 0.47 0.57 0.73 0.47 0.33 0.90 0.77 0.63 0.76 0.93 0.53 0.90 0.70 0.43 0.641 He 0.95 0.91 0.91 0.89 0.82 0.93 0.86 0.86 0.89 0.82 0.91 0.92 0.85 0.88 0.95 0.92 0.84 0.94 0.92 0.72 0.885 PIC 0.94 0.90 0.89 0.97 0.79 0.92 0.83* 0.83 0.87 0.79** 0.90 0.91 0.82 0.86 0.93 0.90 0.80* 0.93 0.90 0.67* 0.868 注: 经Bonferroni校正仍偏离哈迪温伯格平衡(*P<0.05;** P<0.01)Note: Loci deviated from Hardy-Weinberg after Bonferroni correction, * P-value<0.05, ** P-value<0.01 对西昌华吸鳅4个地理种群进行遗传分化指数计算并进行显著性检验(表 3), 结果显示, 水田镇、赤水镇、茅台镇三个种群间无显著分化, 而习水河种群与其他3个种群均存在显著差异(Fst全部大于0.25, P<0.01)。分子方差分析显示(表 4), 遗传变异主要来源于群体内(96.67%), 群体间的遗传变异仅为3.33%。
表 3 西昌华吸鳅4个种群间的遗传分化系数Table 3. Pairwise Fst estimates 4 populations of S. sichangensis种群Population 水田镇ST 赤水镇CSZ 茅台镇MT 习水河XS 水田镇ST — 0.461 0.267 0.000* 赤水镇CSZ 0.02349 — 0.062 0.000* 茅台镇MT 0.02468 0.02749 — 0.000* 习水河XS 0.30812 0.37156 0.26641 — 注: 下三角表示种群间遗传分化系数(Fst); 上三角代表P值, *表示显著分化Note: Fst in below diagonal; P-value in above diagonal, * P-value<0.01 表 4 赤水河西昌华吸鳅分子变异分析Table 4. Analysis of molecular variance (AMOVA) for S. sichangensis变异来源
Resource平方和Sum of squares 变异组合Variance components 变异百分数Percentage variation 群体间Among populations 80.765 0.30840 3.32635 群体内个体间Among individuals within populations 2058.491 8.96312 96.67365 合计Total 2139.256 9.27152 2.3 种群遗传结构
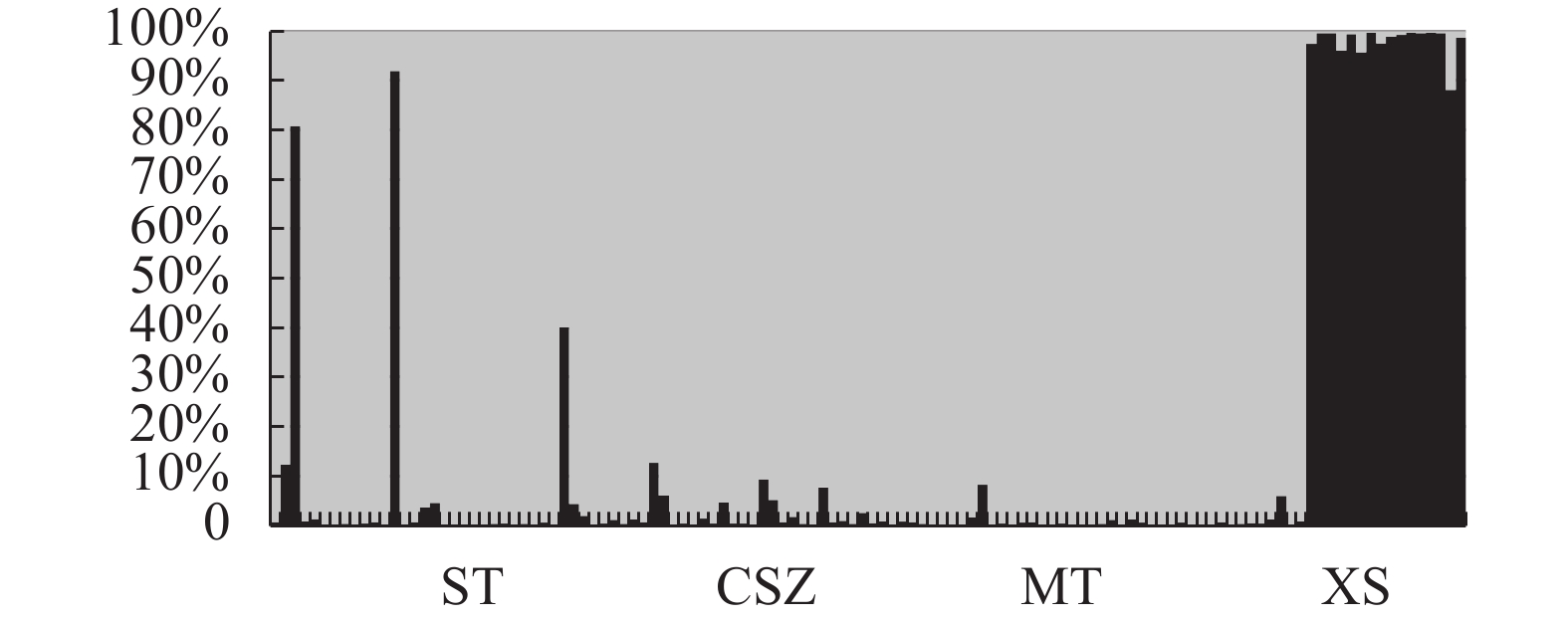
利用Structure软件进行种群结构分析, 计算得出K=2是比较理想的种群亚型类群数目, 即4个种群120尾西昌华吸鳅个体可分为两个亚类群, 如图 2所示, 不同灰度分别代表不同的亚类群, 其中水田镇、赤水镇及茅台镇种群的遗传背景整体趋于一致, 而习水河种群则单独聚于另外一个亚类群, 与遗传分化分析结果相一致。
3. 讨论
3.1 微卫星引物筛选
传统的微卫星分离技术包括小片段DNA克隆法和微卫星富集文库法[25]。随着二代测序技术的发展, 具有通量大、成本低、周期短特点的高通量测序对基因组进行随机测序即可获得大量的微卫星序列, 相比传统方法在获取微卫星序列方面展现出了突出的优势[26, 27]。特别是对于西昌华吸鳅这类DNA序列数据较为贫乏的物种, 利用高通量测序获取微卫星序列的技术难度减小且效率大幅提高。因此, 高通量测序法必将逐步取代传统方法, 成为微卫星标记开发领域的主流。
3.2 西昌华吸鳅种群遗传学特征
生物多样性包括遗传多样性、物种多样性和生态系统多样性, 其中遗传多样性既是物种多样性和生态系统多样性的基础, 也是生物多样性的核心和重要组成部分。杂合度是描述群体遗传学上的群体多态性, 当杂合度在0.5到0.8之间即可认为该群体具有较高的多样性[28]。在本研究中, 西昌华吸鳅在赤水河及其支流的4个种群的观测杂合度值均大于0.5, 表明各种群遗传多样性现状均处于较高水平。多态信息含量也是衡量基因片段多态性的理想指标, Botstein等[29]认为当PIC>0.5时, 该位点即为高度多态位点。本实验中各种群PIC均大于0.5, 表明西昌华吸鳅各种群遗传多样性高, 说明这些种群种质资源良好, 具有一定的种群稳定性。
3.3 西昌华吸鳅种群分化与遗传特征
遗传分化指数Fst是揭示种群间遗传分化程度的重要参数。Wright[30]认为: 若种群间Fst<0.05, 则表明种群间无分化; 若0.05<Fst<0.15, 则表明种群间存在中度分化; 若0.15<Fst<0.25, 则为高度分化。在本研究中, 赤水河干流水田、赤水镇、茅台种群间遗传分化指数均小于0.05, 表明干流种群间无显著分化; 而习水河种群与干流种群Fst均大于0.25, 存在高度分化。种群遗传结构分析结果同样与上述结果一致, 习水河种群单独聚为一个亚类群, 而干流种群遗传背景趋于一致, 聚为另一个亚类群。
西昌华吸鳅与四川华吸鳅相似, 产微黏性卵, 在自然条件下常黏附于河流激流砾石滩上完成胚胎发育过程, 由于黏性较弱, 受水流冲击后常脱离基质顺水漂流[31]。习水河与赤水河交汇于赤水河下游近河口处, 与赤水河上游和中游种群难以进行基因交流, 进而逐渐分化成独立的亚群。
西昌华吸鳅是我国长江上游地区的特有类群, 具有重要的遗传价值和生态价值。近年来野外调查也发现西昌华吸鳅的种群规模呈下降趋势。因此, 在今后的管理中仍应加大赤水河水质的保护力度, 为长江上游特有水生生物资源提供良好的栖息环境。
致谢:
感谢中国科学院水生生物研究所王雪、张富斌、秦强在野外采样给予的帮助。
-
表 1 西昌华吸鳅微卫星位点及PCR引物信息
Table 1 Information of polymorphic microsatellite markers of S. sichangensis
位点Loci 引物序列Primer sequence (5′-3′) 重复单元
Repeat motif片段大小
Size range (bp)退火温度Tm (℃) SS010 TGACTGATGCATGACGGACT GCAAAATGTGCTGCAAGACG (TGTA)22 223—310 55 SS017 CGTGATGAAAAACTGCTGCG TCACTCGTTCGCTCATTCACT (TTCA)11 97—140 56 SS018 GCACCACCCATCTGTTGTTG AATCCCACAGCTTTTTCACACA (ACAT)11 128—171 54 SS025 GTCCAAAATATCATTTAGCCCAGCA AAGGTGGATGGAGGGAAATCTG (CTGT)21 74—157 53 SS030 ATCCTGAGCTGTCGCCTTAC CAGCGTGCGCCCTAGTTTTA (AACA)10 263—302 60 SS036 TGCAGAATGAGGTGGACACA ATCAAACTCACAGCTAGGCAG (TGTT)9 248—283 55 SS042 GTTTGGCACAGATCTCGGTT AAAGTCATAAATCCTGGACAGTT (TTCT)28 164—275 53 SS045 CACCCGTCTCACAACATGAC ATGCAGCTTTGGCATTGCAC (GAT)14 161—202 55 SS050 CACGTGTGATCGCAGACAAA GGGAAGGCTTGCTTTACCTTCT (ATA)10 84—113 58 SS051 AGGTTTGGGATAAGTTCAGGGAC TAACAGATTCCATCCAGGGCT (ACA)10 252—281 55 SS053 AGCTCTTAAATAGGCCAAGTGTT AAGGTGGTGGTGTTAAGGTGT (GATA)23 134—225 55 SS055 AAAACCCTACACACCCTGCTT GGCTGCTCATGCAAACCAAT (GATA)22 109—196 55 SS061 TTAAACTGACCGGCGAGCAA TGTATGTGCAGGATGAGAGCG (TCC)11 119—151 56 SS063 GTGCGCCTCGTTGATCTTCT AAAAACAGCGTGACGTGGATG (GAA)11 151—183 55 SS064 CTATATATAAGCGACGCCGAGC ACTGCTCTTTACGTCCTCTGG (AGA)26 105—182 57 SS066 TTGCGGCTGTACGCAGAAT CGGGATGCGGATGACTACAG (CAA)12 73—108 56 SS073 TGATTGCCCAGGTGTGTGTT ACACCTGTTCAGTGAATCATCC (AAT)11 195—227 51 SS075 GCAGAAAGGTCAGTGTAAGGGA CCACAGACTGCACTTGCACA (AAT)11 181—213 54 SS080 TGTTAATCTGCTGCCGTGGG GGAGCGGGTTAAGAAGACACT (GCGT)9 174—209 55 SS083 GCTGATACCTGTTTAGCTGTTGC TCCACTCCGTTAGATGAGGTC (GATA)44 125—300 57 SS090 GCAGTAGGCAATTTGCAATAAGT ATCCACACACACACGACTGG (TATC)41 95—258 53 SS091 GACATTCCCTGATGCGGACA TTGCCACAGTCAAAGTGGGT (CTGT)10 124—163 58 SS108 GTTTGCGCTTTCTGTGCTGA AAGCAACGTCTTTCGGATGC (GACA)9 205—240 55 SS109 TCGTTGTCGTGTAAACAGCC CCGTACAGGTGCATGTGACT (TAT)10 73—102 58 SS110 GCAGAATGTGCACCTTGGAAA ATTGCTGCACATTAGAAGTGG (ATAC)11 128—171 53 SS112 ACTTTCATGGCATGTGGTGTG TCACACGAAGTGAACTGCCA (ATCT)12 83—130 51 SS116 GTCTCTGCTGAGGCAATTCG CGCCCATCACTACCGATAACT (TGA)14 204—245 55 SS129 TGTGCTGGACAAACATGCTG AGGTCAAAGGTTAGTGTTGGGT (TCA)20 211—258 53 SS144 CAGCACAAGTGGAAGAACACTTT AAAGACCAGTTTAATGGGAGCA (ATAG)12 79—126 54 注: 全部位点信息已上传至GenBank, 登录号为MH745718—MH745746Note: Information of all loci was submitted to GenBank (Accession numbers: MH745718—MH745746) 表 2 西昌华吸鳅4个种群微卫星标记的遗传学特征
Table 2 Characteristics of the 20 microsatellite loci in 4 populations of S. sichangensis
种群
Population位点Loci Mean SS10 SS17 SS25 SS36 SS45 SS53 SS61 SS63 SS73 SS75 SS80 SS90 SS108 SS110 SS112 SS116 SS129 SS144 SS109 SS51 ST Na 23 17 21 10 10 17 9 13 13 15 23 19 8 13 22 13 8 17 17 10 14.9 Ho 0.75 0.55 0.80 0.45 0.62 0.48 0.47 0.53 0.57 0.83 0.35 0.77 0.76 0.45 0.80 0.90 0.69 0.90 0.62 0.69 0.649 He 0.95 0.93 0.94 0.86 0.83 0.92 0.83 0.86 0.87 0.89 0.95 0.94 0.82 0.89 0.95 0.91 0.81 0.94 0.92 0.78 0.890 PIC 0.93 0.91 0.93 0.84** 0.80 0.90 0.80* 0.84 0.85 0.86 0.93 0.92 0.79 0.86 0.93 0.89 0.78 0.93 0.90 0.74 0.867 CSZ Na 28 16 19 11 11 21 7 11 9 13 22 15 10 15 19 12 11 14 19 7 14.5 Ho 0.80 0.77 0.86 0.66 0.83 0.45 0.32 0.70 0.73 0.80 0.63 0.90 0.90 0.43 0.87 0.70 0.33 0.53 0.69 0.48 0.669 He 0.95 0.92 0.92 0.86 0.85 0.95 0.78 0.89 0.88 0.89 0.95 0.91 0.85 0.88 0.94 0.89 0.83 0.89 0.93 0.78 0.887 PIC 0.94 0.90 0.90 0.83 0.83 0.93 0.74* 0.87* 0.76 0.87 0.94 0.89 0.83 0.86* 0.93 0.87* 0.80** 0.87 0.91 0.74** 0.861 MT Na 24 18 18 10 9 21 8 10 15 16 13 20 9 17 19 14 9 23 12 7 14.6 Ho 0.87 0.45 0.59 0.64 0.37 0.48 0.47 0.40 0.50 0.37 0.20 0.87 0.53 0.40 0.87 0.73 0.53 0.67 0.10 0.35 0.520 He 0.95 0.90 0.93 0.81 0.77 0.95 0.82 0.79 0.89 0.88 0.70 0.95 0.85 0.92 0.94 0.89 0.84 0.94 0.89 0.72 0.867 PIC 0.93 0.88** 0.91 0.78 0.74* 0.94 0.78 0.75** 0.87 0.86** 0.68** 0.93 0.82 0.90 0.92 0.86 0.80* 0.92 0.87** 0.68** 0.841 XS Na 26 16 19 13 10 20 10 9 12 11 15 19 10 11 20 12 8 19 15 8 14.1 Ho 0.70 0.73 0.57 0.70 0.67 0.33 0.47 0.57 0.73 0.47 0.33 0.90 0.77 0.63 0.76 0.93 0.53 0.90 0.70 0.43 0.641 He 0.95 0.91 0.91 0.89 0.82 0.93 0.86 0.86 0.89 0.82 0.91 0.92 0.85 0.88 0.95 0.92 0.84 0.94 0.92 0.72 0.885 PIC 0.94 0.90 0.89 0.97 0.79 0.92 0.83* 0.83 0.87 0.79** 0.90 0.91 0.82 0.86 0.93 0.90 0.80* 0.93 0.90 0.67* 0.868 注: 经Bonferroni校正仍偏离哈迪温伯格平衡(*P<0.05;** P<0.01)Note: Loci deviated from Hardy-Weinberg after Bonferroni correction, * P-value<0.05, ** P-value<0.01 表 3 西昌华吸鳅4个种群间的遗传分化系数
Table 3 Pairwise Fst estimates 4 populations of S. sichangensis
种群Population 水田镇ST 赤水镇CSZ 茅台镇MT 习水河XS 水田镇ST — 0.461 0.267 0.000* 赤水镇CSZ 0.02349 — 0.062 0.000* 茅台镇MT 0.02468 0.02749 — 0.000* 习水河XS 0.30812 0.37156 0.26641 — 注: 下三角表示种群间遗传分化系数(Fst); 上三角代表P值, *表示显著分化Note: Fst in below diagonal; P-value in above diagonal, * P-value<0.01 表 4 赤水河西昌华吸鳅分子变异分析
Table 4 Analysis of molecular variance (AMOVA) for S. sichangensis
变异来源
Resource平方和Sum of squares 变异组合Variance components 变异百分数Percentage variation 群体间Among populations 80.765 0.30840 3.32635 群体内个体间Among individuals within populations 2058.491 8.96312 96.67365 合计Total 2139.256 9.27152 -
[1] 乐佩琦. 中国动物志: 鲤形目(下卷). 北京: 科学出版社. 2000, 558—560 Yue P Q. Fauna Sinica, Osteichthyes, Cypriniformes III [M]. Beijing: Science Press. 2000, 558—560
[2] 吴金明, 赵海涛, 苗志国, 等. 赤水河鱼类资源的现状与保护. 生物多样性, 2010, 18(2): 162—168 Wu J M, Zhao H T, Miao Z G, et al. Status and conservation of fish resources in the Chishui River [J]. Biodiversity Science, 2010, 18(2): 162—168
[3] Liu S W, Chen X Y, Yang J X. Two new species and a new record of the genus Sinogastromyzon, (Teleostei: Balitoridae) from Yunnan, China [J]. Environmental Biology of Fishes, 2010, 87(1): 25 doi: 10.1007/s10641-009-9554-8
[4] 陈宜瑜. 中国平鳍鳅科鱼类系统分类的研究Ⅰ.平鳍鳅亚科鱼类的分类. 水生生物学报, 1978, 6(3): 331—348 Chen Y Y. Systematic studies on the fishes of the family Homalopteridae of China Ⅰ [J]. Aca Hydrobiologica Sinica, 1978, 6(3): 331—348
[5] Kottelat M, Chu X L. A synopsis of Chinese balitorine loaches (Osteichthyes: Homalopteridae) with comments on their phylogeny and description of a new genus [J]. Revue Suisse De Zoologie, 1988, 1(95): 181—201
[6] 唐文乔, 陈宜瑜. 平鳍鳅科鱼类的分类学研究. 上海海洋大学学报, 2000, 9(1): 1—10 doi: 10.3969/j.issn.1004-7271.2000.01.001 Tang W Q, Chen Y Y. Study on taxonomy of Homalopteridae [J]. Journal of Shanghai Fisheries University, 2000, 9(1): 1—10 doi: 10.3969/j.issn.1004-7271.2000.01.001
[7] 邓其祥. 雅砻江下游地区的鱼类区系和分布. 动物学杂志, 1996, (5): 5—12 Deng Q X. Fish fauna and distribution in the lower reaches of Yalong River [J]. Chinese Journal of Zoology, 1996, (5): 5—12
[8] 张庆, 周伟, 潘晓赋, 等. 滇西北中甸地区的鱼类. 陕西师范大学学报(自科版), 2002, (s1): 170—175 Zhang Q, Zhou W, Pan X F, et al. The ichthyofauna of Zhongdian area in northwest Yunnan [J]. Journal of Shanxi Normal University (
Natural Science Edition ) , 2002, (s1): 170—175 [9] Park Y S, Brosse S. Conservation strategies for endemic fish species threatened by the Three Gorges Dam [J]. Conservation Biology, 2003, 17(6): 1748—1758 doi: 10.1111/cbi.2003.17.issue-6
[10] 代应贵, 李敏. 梵净山及邻近地区鱼类资源的现状. 生物多样性, 2006, 14(1): 55—64 doi: 10.3321/j.issn:1005-0094.2006.01.007 Dai Y G, Li M. Fish resources around Fanjing Mountain, Guizhou [J]. Biodiversity Science, 2006, 14(1): 55—64 doi: 10.3321/j.issn:1005-0094.2006.01.007
[11] Tang Q Y, Liu S Q, Yu D, et al. Mitochondrial capture and incomplete lineage sorting in the diversification of balitorine loaches (Cypriniformes, Balitoridae) revealed by mitochondrial and nuclear genes [J]. Zoologica Scripta, 2012, 41(3): 233—247 doi: 10.1111/zsc.2012.41.issue-3
[12] Liu S, Mayden R L, Zhang J, et al. Phylogenetic relationships of the Cobitoidea (Teleostei: Cypriniformes) inferred from mitochondrial and nuclear genes with analyses of gene evolution [J]. Gene, 2012, 508(1): 60—72 doi: 10.1016/j.gene.2012.07.040
[13] Randall Z S, Page L M. On the paraphyly of Homaloptera (Teleostei: Balitoridae) and description of a new genus of hillstream loaches from the Western Ghats of India [J]. Zootaxa, 2015, 3926(1): 57—86 doi: 10.11646/zootaxa.3926.1
[14] 李小娟. 长江上游金沙鳅属和华吸鳅属鱼类物种分化的比较研究. 中国科学院大学, 北京. 2014 Li X J. Speciation of two fish genera Jinshaia and Sinogastromyzon (Cyprinformes: Balitoridae) in Upper Yangtze River [D]. Thesis for Master of Science. University of Chinese Academy of Sciences, Beijing. 2014.
[15] Selkoe K A, Toonen R J. Microsatellites for ecologists: a practical guide to using and evaluating microsatellite markers [J]. Ecology Letters, 2006, 9(5): 615—629 doi: 10.1111/ele.2006.9.issue-5
[16] Aljanabi S M, Martinez I. Universal and rapid salt-extraction of high quality genomic DNA for PCR-based techniques [J]. Nucleic Acids Research, 1997, 25(22): 4692—4693 doi: 10.1093/nar/25.22.4692
[17] Ye J, Coulouris G, Zaretskaya I, et al. Primer-BLAST: A tool to design target-specific primers for polymerase chain reaction [J]. BMC Bioinformatics, 2012, 13(1): 134—134 doi: 10.1186/1471-2105-13-134
[18] Glaubitz J C. CONVERT: a user-friendly program to reformat diploid genotypic data for commonly used population genetic software packages [J]. Molecular Ecology Notes, 2004, 4(2): 309—310 doi: 10.1111/men.2004.4.issue-2
[19] Van Oosterhout C, Hutchinson W F, Wills D, et al. micro-checker: software for identifying and correcting genotyping errors in microsatellite data [J]. Molecular Ecology Notes, 2004, 4(3): 535—538 doi: 10.1111/men.2004.4.issue-3
[20] Rousset F. Genepop’007: a complete re‐implementation of the genepop software for Windows and Linux [J]. Molecular Ecology Resources, 2008, 8(1): 103—106 doi: 10.1111/j.1471-8286.2007.01931.x
[21] Marshall T C, Slate J, Kruuk L E, et al. Statistical confidence for likelihood-based paternity inference in natural populations [J]. Molecular Ecology, 1998, 7(5): 639—655 doi: 10.1046/j.1365-294x.1998.00374.x
[22] Excoffier L, Lischer H E L. Arlequin suite ver 3.5: a new series of programs to perform population genetics analyses under Linux and Windows [J]. Molecular Ecology Resources, 2010, 10(3): 564 doi: 10.1111/men.2010.10.issue-3
[23] Pritchard J K, Stephens M, Donnelly P, et al. Inference of population structure using multilocus genotype data [J]. Genetics, 2000, 155(2): 945—959
[24] PorrasHurtado L, Ruiz Y, Santos C, et al. An overview of Structure: applications, parameter settings, and supporting software [J]. Frontiers in Genetics, 2013, 4(98): 98
[25] 孙效文, 贾智英, 魏东旺, 等. 磁珠富集法与小片段克隆法筛选鲤微卫星的比较研究. 中国水产科学, 2005, 12(2): 126—132 doi: 10.3321/j.issn:1005-8737.2005.02.003 Sun X W, Jia Z Y, Wei D W, et al. Comparison between magnetic beads enriched and small inserted fragment library for microsatellite sequences of common carp [J]. Journal of Fishery Sciences of China, 2005, 12(2): 126—132 doi: 10.3321/j.issn:1005-8737.2005.02.003
[26] 杨兵, 林琳, 李纯厚, 等. 基于高通量测序的二长棘鲷微卫星标记开发与评价. 南方水产科学, 2015, 11(4): 116—120 doi: 10.3969/j.issn.2095-0780.2015.04.017 Yang B, Lin L, Li C H, et al. Development and evaluation of microsatellite markers in Parargyrops edita [J]. South China Fisheries Science, 2015, 11(4): 116—120 doi: 10.3969/j.issn.2095-0780.2015.04.017
[27] 高峰涛, 邵长伟, 崔忠凯, 等. 基于高通量测序的青石斑鱼基因组微卫星开发及评价. 中国海洋大学学报(自然科学版), 2017, 47(4): 52—57 Gao F T, Shao C W, Cui Z K, et al. Development and population genetic diversity analysis of microsatellite markers in Epinephelus awoara [J]. Periodical of Ocean University of China, 2017, 47(4): 52—57
[28] Takezaki N, Nei M. Genetic distances and reconstruction of phylogenetic trees from microsatellite DNA [J]. Genetics, 1996, 144(1): 389—399
[29] Botstein D, White R L, Skolnick M, et al. Construction of a genetic linkage map in man using restriction fragment length polymorphisms [J]. American Journal of Human Genetics, 1980, 32: 314—331
[30] Wright S. The interpretation of population structure by F-statistics with special regard to systems of mating [J]. Evolution, 1965, 19(3): 395—420 doi: 10.1111/evo.1965.19.issue-3
[31] 吴金明, 王芊芊, 刘飞, 等. 赤水河四川华吸鳅的早期发育. 四川动物, 2011, 30(4): 527—529 doi: 10.3969/j.issn.1000-7083.2011.04.002 Wu J M, Wang Q Q, Liu F, et al. Early development of Sinogastromyzon szechuanensis in the Chishui River [J]. Sichuan Journal of Zoology, 2011, 30(4): 527—529 doi: 10.3969/j.issn.1000-7083.2011.04.002
-
期刊类型引用(6)
1. 崔学海,沙航,曹继增,郜卫华,梁宏伟. 克氏原螯虾湖北7个养殖群体遗传多样性的SSR分析. 淡水渔业. 2024(06): 79-86 .  百度学术
百度学术
2. 张芹,王延晖,王冰柯,屈长义,刘英杰. 基于基因组微卫星的团头鲂养殖群体遗传多样性分析和指纹图谱构建. 安徽农业科学. 2023(08): 99-104 .  百度学术
百度学术
3. 许珊华,章嘉淇,卢婷,符圆,唐潇,唐琼英,夏正龙,蔡缪荧,高权新,李景芬,杨国梁. 基于微卫星标记的不同种质资源罗氏沼虾遗传多样性研究. 江苏农业科学. 2021(06): 45-51 .  百度学术
百度学术
4. 王锦秀,任道全,王新月,陈生熬,宋勇. 塔里木河流域5个地理种群的叶尔羌高原鳅遗传多样性分析. 渔业科学进展. 2021(04): 46-54 .  百度学术
百度学术
5. 王锦秀,宋勇,王新月,陈生熬,任道全. 基于de novo高通量测序的叶尔羌高原鳅微卫星位点筛选与多态性分析. 塔里木大学学报. 2020(02): 25-32 .  百度学术
百度学术
6. 李景芬,夏正龙,栾生,蔡缪荧,罗坤,唐琼英,高权新,孔杰,杨国梁. 五个罗氏沼虾群体遗传多样性的微卫星分析. 水生生物学报. 2020(06): 1208-1214 .  本站查看
本站查看
其他类型引用(8)



 下载:
下载: